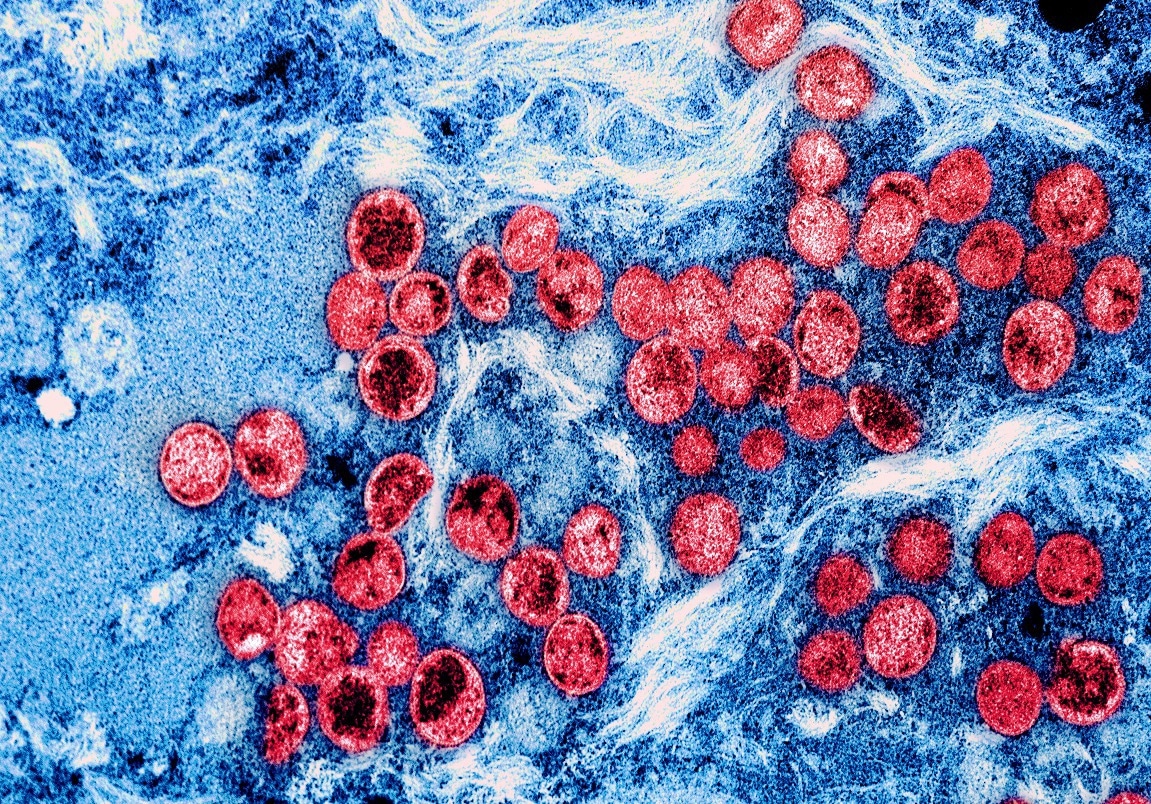
В недавнем исследовании, опубликованном на сервере препринтов bioRxiv* , группа исследователей из Индии проанализировала последовательности полного генома вируса обезьяньей оспы, выделенного от пациентов с обезьяньей оспой, путешествующих за границу и не путешествующих за границу, чтобы понять филогенетические отношения и геномную эволюцию вируса, которые могут способствуют более высокой скорости передачи.
Исследование: Характеристика генома случаев оспы обезьян, выявленных в Индии: идентификация трех субкластеров среди линии A.2 . Кредит изображения: НИАИД
Фон
Вирус обезьяньей оспы, как и вызывающий оспу вирус натуральной оспы , является разновидностью ортопоксвирусов, принадлежащих к семейству Poxviridae . Это двухцепочечный вирус дезоксирибонуклеиновой кислоты (ДНК), геном которого кодирует около 190 генов.
Первый известный случай оспы обезьян у человека был зарегистрирован в 1970 году в Демократической Республике Конго, который распространился на страны Западной и Центральной Африки с последующими вспышками в Соединенных Штатах (США) в 2003 году и Соединенном Королевстве (Великобритания) в 2018 году. Исследования генома, проведенные Всемирной организацией здравоохранения (ВОЗ), выявили две основные клады — кладу I (кладу бассейна Конго) и кладу II (кладу Западной Африки) с двумя субкладами в кладе II. Глобальная вспышка оспы обезьян в 2022 году была связана с Clade IIb.
Вирусы из семейства Poxviridae демонстрируют высокую частоту межвидовой и внутривидовой рекомбинации. Клады I и II имели генетическое расстояние 900 п.н. Генетические изменения могут предоставить вирусу преимущества в плане передачи и заражения. Таким образом, анализ всего генома циркулирующих штаммов вируса оспы обезьян имеет важное значение для эпиднадзора за заболеванием.
Об исследовании
В настоящем исследовании были собраны образцы мазков из носоглотки и ротоглотки, корок поражений и жидкостей от 96 человек с подозрением на оспу обезьян. Положительные случаи были идентифицированы на основе полимеразной цепной реакции (ПЦР) в реальном времени с использованием праймеров, специфичных для оспы обезьян.

California Gold Nutrition, Immune 4, средство для укрепления иммунитета, 60 вегетарианских капсул
Окончательный набор образцов включал пять образцов из Кералы (с историей международных поездок) и пять образцов из Дели (без истории недавних международных поездок). Отрицательные образцы были дополнительно проверены на наличие энтеровируса и вируса ветряной оспы.
Секвенирование следующего поколения использовалось для геномной характеристики положительных образцов. Кроме того, был проведен филогенетический анализ окончательного набора данных, состоящего из последовательностей генома, созданных в этом исследовании, и 75 последовательностей из баз данных NCBI (Национальный центр биотехнологической информации) и GISAID (Глобальная инициатива по обмену данными о птичьем гриппе), которые были созданы до начала исследования. и вспышка оспы обезьян после 2022 года.
Полученные результаты
В ходе исследования было извлечено от 90% до 99% генома обезьяньей оспы из корки поражения и образцов жидкости из всех положительных случаев. Филогенетические деревья поместили 10 образцов из Индии в линию Clade IIb A.2 вместе с восемью другими образцами из США, Таиланда и Великобритании.
Анализ на основе генома разделил линию A.2 на три субкластера, с семью последовательностями (пять из Кералы и две из Дели), ответвляющимися со штаммами UK-2022 OP331335.1 и USA-2022 ON674051.1 и образующими один подкластер. Определяющие линию мутации в положениях C 179537 T, C 25072 T и A 140492 C дополнительно классифицировали пять последовательностей из Кералы как подлинию A.2.1.
Остальные три последовательности из Дели разветвились со штаммом USA-2022 ON675438.1 и образовали второй субкластер. Третий подкластер состоял из последовательностей из других штаммов США и Великобритании и образцов из Таиланда.
Исследования связывают кратковременную эволюцию вируса оспы обезьян с мутациями в генах комплекса редактирования аполипопротеина В (APOBEC3), которые приводят к активности цитидиндезаминазы. Анализ генома в настоящем исследовании выявил 13 новых мутаций APOBEC3 и 16 однонуклеотидных полиморфизмов (SNP), которые, по мнению авторов, являются определяющими линию изменениями в линии A.2. Исследование также выявило 25 дополнительных мутаций APOBEC3 в штаммах обезьяньей оспы, циркулирующих в Индии.
Последовательности оспы обезьян из Индии расходились с более ранними линиями, такими как B.1 из европейских стран, таких как Германия, Италия и Франция, и линия A.1 2017-2018 гг. из Нигерии, Сингапура и Израиля.
Выводы
Подводя итог, исследование сообщает о 13 новых мутациях в гене APOBEC3 вируса оспы обезьян, которые потенциально могут быть вовлечены в эволюцию вируса. Кроме того, результаты также выявили 16 новых SNP, которые, наряду с мутациями APOBEC3, привели к тому, что образцы из Индии сформировали линию A.2.1. Авторы считают, что мутации в генах ортопоксвируса связаны с повышенной вирулентностью за счет подавления иммунитета у хозяина.
Кроме того, гены в терминальной области вируса оспы обезьян и других видов ортопоксвирусов ответственны за адаптацию и передачу хозяина. Таким образом, полногеномные исследования для понимания роли этих генов и наблюдения за возникающими мутациями необходимы для сдерживания распространения оспы обезьян.
*Важное замечание
bioRxiv публикует предварительные научные отчеты, которые не рецензируются экспертами и, следовательно, не должны рассматриваться как окончательные, направляющие клиническую практику/поведение, связанное со здоровьем, или рассматриваться как установленная информация.
















Оставить Комментарий
Вы должны войти, чтобы оставить комментарий.